近日,Star Protocols在线发表了中国科学院上海营养与健康研究所题为Detecting archaic introgression and modeling multiple-wave admixture with ArchaicSeeker 2.0的研究成果。该工作提供了ArchaicSeeker 2.0方法的具体分析流程(如图)。ArchaicSeeker 2.0方法主要用于检测现代人类基因组中由古人类渗入的片段,并进而重构现代人类与古人类之间的种群交融历史模型。
现代人类与古人类在漫长的演化历史中存在着错综复杂的基因交流关系。由于现代人群中目前所保留的基因渗入比例较低且渗入时间较为久远等因素,以往用于检测古人类对现代人类基因渗入片段的方法大都未取得良好效果,此外,精细化重构现代人类与古人类之间的基因交流历史模型也存在较大难度。ArchaicSeeker 2.0可针对性地解决此类问题,有效检测和量化近缘种的基因交流,并在更精细的尺度上重构复杂的基因交流历史。该方法主要由三个功能模块组成:搜寻潜在的基因渗入片段、将渗入片段匹配至对应的祖先人群和构建遗传渐渗历史模型。此前关于ArchaicSeeker 2.0方法的介绍参见http://www.sinh.cas.cn/xwgg/kyjz/202111/t20211102_6240465.html。
该研究中的protocol以公共开放数据库中的中国汉族人群21号和22号染色体数据为例,展示了利用ArchaicSeeker 2.0 方法检测和量化其由古人类尼安德特人和丹尼索瓦人渗入的基因组片段,并进而重构丹尼索瓦人对中国汉族人群的基因渐渗历史模型的分析流程,包括分析流程中每一步需要准备的输入文件格式、注意事项、代码执行命令以及对应的输出文件格式。此外,protocol还列举了用户在安装和使用ArchaicSeeker 2.0方法时可能遇到的代码报错信息或者文件格式问题,并提供了对应的解决方案,为用户的分析工作提供了便利。
研究工作得到国家自然科学基金委员会、中科院战略性先导科技专项、英国皇家学会牛顿基金、上海市科委等的资助。
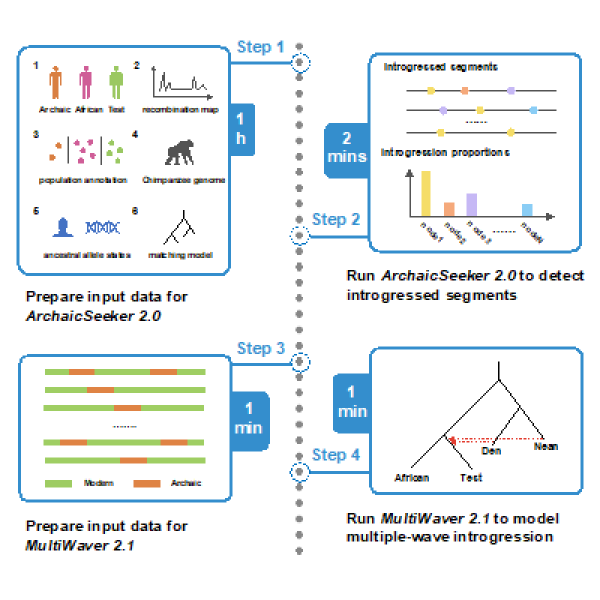
ArchaicSeeker 2.0 分析流程图




